Topologisch assoziierte Domäne: Unterschied zwischen den Versionen
K (dc name tag added) |
|||
| (5 dazwischenliegende Versionen von einem anderen Benutzer werden nicht angezeigt) | |||
| Zeile 1: | Zeile 1: | ||
''Synonym: TAD''<br> | ''Synonym: TAD''<br> | ||
'''''Englisch''': topologically associating domain'' | '''''Englisch''': <name lang="en">topologically associating domain</name>'' | ||
== Definition == | == Definition == | ||
| Zeile 20: | Zeile 20: | ||
Die chromosomale Organisation in TADs wird durch den [[Loop-Extrusion]]-Prozess erreicht, der durch [[Cohesin]] vermittelt wird. Die Extrusion kommt durch den Transkriptionsrepressor [[CTCF]] zum Halt, wodurch stabile Schleifen gebildet werden. Dadurch werden [[Enhancer]]-[[Promoter]]-[[Interaktion]]en und [[Replikation]]seinheiten reguliert. | Die chromosomale Organisation in TADs wird durch den [[Loop-Extrusion]]-Prozess erreicht, der durch [[Cohesin]] vermittelt wird. Die Extrusion kommt durch den Transkriptionsrepressor [[CTCF]] zum Halt, wodurch stabile Schleifen gebildet werden. Dadurch werden [[Enhancer]]-[[Promoter]]-[[Interaktion]]en und [[Replikation]]seinheiten reguliert. | ||
== | == Klinik == | ||
Strukturelle Variationen innerhalb der TADs können die Dosierung von Enhancern verändern und somit sequenzabhängig zum Verlust oder zur Verstärkung der Funktion ihrer [[endogen]]en [[Zielgen]]e führen. | Strukturelle Variationen innerhalb der TADs können die Dosierung von Enhancern verändern und somit sequenzabhängig zum Verlust oder zur Verstärkung der Funktion ihrer [[endogen]]en [[Zielgen]]e führen. | ||
Zu den [[Erkrankung]]en, die mit intra-TAD Variationen in Verbindung stehen, zählen: | Zu den [[Erkrankung]]en, die mit intra-TAD-Variationen in Verbindung stehen, zählen: | ||
* [[Kolorektalkarzinom]] | * [[Kolorektalkarzinom]] | ||
* [[Plattenepithelkarzinom]] der [[Lunge]] | * [[Plattenepithelkarzinom]] der [[Lunge]] | ||
Aktuelle Version vom 21. März 2024, 09:56 Uhr
Synonym: TAD
Englisch: topologically associating domain
Definition
Hintergrund
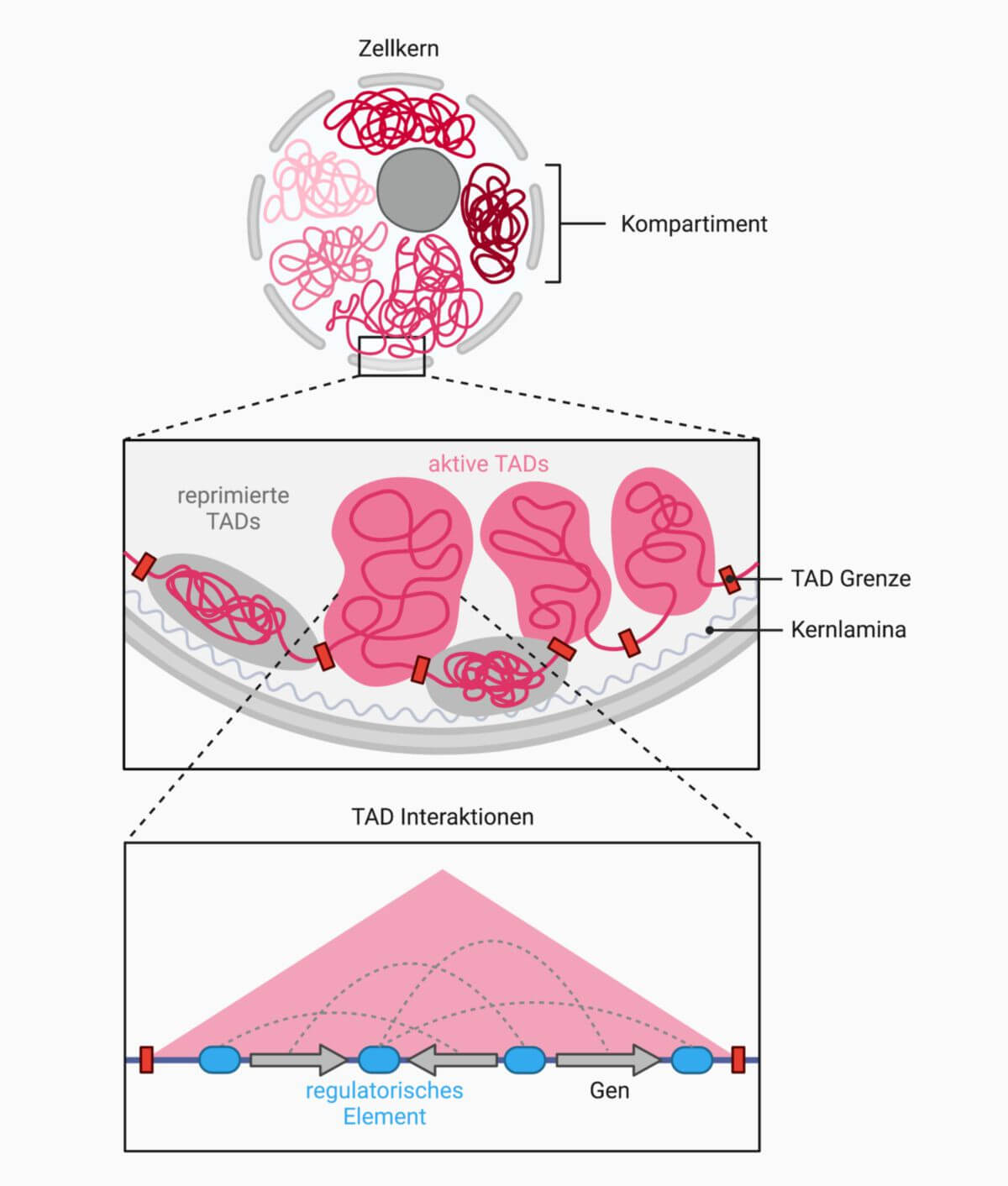
Chromosomen sind hierarchisch in große Kompartimente gegliedert, die wiederum aus topologisch assoziierten Domänen bestehen. Auf Grundlage des Transkriptions- oder Chromatinstatus assoziieren DNA-Sequenzen in Domänen mit ähnlichen Eigenschaften. Dadurch werden Kompartimente gebildet, die überwiegend transkriptionell aktiv oder still sind.
TADs interagieren bevorzugt mit sich selbst und nicht mit anderen Regionen des Genoms.
Einteilung
DNA-Sequenzen der aktiven Domäne enthalten aktivierende Histonmodifikationen. Trotzdem ist es möglich, dass bestimmte Regionen nicht transkribiert werden. Aktives Euchromatin befindet sich eher im Zentrum des Zellkerns.
Analog dazu enthalten stille Domänen inaktivierende Histonmodifikationen, die mit einem transkriptionell reprimierten Zustand verbunden sind. Inaktives Heterochromatin befindet sich in der Peripherie des Zellkerns (Lamina-assoziierte Domänen) oder des Nukleolus (Nukleolus-assoziierte Domänen).
Entstehung
Die chromosomale Organisation in TADs wird durch den Loop-Extrusion-Prozess erreicht, der durch Cohesin vermittelt wird. Die Extrusion kommt durch den Transkriptionsrepressor CTCF zum Halt, wodurch stabile Schleifen gebildet werden. Dadurch werden Enhancer-Promoter-Interaktionen und Replikationseinheiten reguliert.
Klinik
Strukturelle Variationen innerhalb der TADs können die Dosierung von Enhancern verändern und somit sequenzabhängig zum Verlust oder zur Verstärkung der Funktion ihrer endogenen Zielgene führen.
Zu den Erkrankungen, die mit intra-TAD-Variationen in Verbindung stehen, zählen:
- Kolorektalkarzinom
- Plattenepithelkarzinom der Lunge
- Medulloblastom
- mesomele Dysplasie
- Cooks-Syndrom
- Liebenberg-Syndrom
Strukturelle Variationen, welche die TAD-Grenzen überschreiten (inter-TAD), haben das Potenzial, Chromosomkompartimente zu unterbrechen und neue regulatorische Einheiten zu schaffen. Dies ist ein häufiges Phänomen bei der Krebsentwicklung. Bei der akuten lymphoblastischen T-Zell-Leukämie (T-ALL) werden beispielsweise durch wiederkehrende Mikrodeletionen CTCF-assoziierte Domänengrenzen entfernt, was die Aktivierung von Protoonkogenen ermöglicht.
Quellen
- Moraru und Schalch Chromatin fiber structural motifs as regulatory hubs of genome function? Essays in biochemistry 2019</ref>
- Rowley und Corces Organizational principles of 3D genome architecture Nat Rev Genet 2018
- Spielmann et al. Structural variation in the 3D genome Nat Rev Genet 2018